Factores genéticos y fisuras orofaciales no sindrómicas
Genetic Factors and Nonsyndromic Orofacial Clefts
DOI:
https://doi.org/10.15446/revfacmed.v64n2.53551Palabras clave:
Labio leporino, Fisura del paladar, Etiología, Genética (es)Cleft lip, Cleft palate, Etiology, Genetics (en)
carta al editor
DOI: https://doi.org/10.15446/revfacmed.v64n2.53551
Factores genéticos y fisuras orofaciales no sindrómicas
Genetic Factors and Nonsyndromic Orofacial Clefts
Marcos Roberto Tovani-Palone1 • Vivian Patricia Saldias-Vargas1
Recibido: 13/10/2015 Aceptado: 13/01/2016
1 Universidade de São Paulo - Hospital de Reabilitação de Anomalias Craniofaciais - Bauru - Brasil.
Correspondencia: Marcos Roberto Tovani-Palone. Seção de Odontopediatria e Saúde Coletiva, Hospital de Reabilitação de Anomalias Craniofaciais, Universidade de São Paulo. Rua Silvio Marchione 3-20, Vila Universitária CEP 17012-900. Teléfono: +55 14 3235-8141; Fax: +55 14 3234-7818. Bauru. Brasil. Correo electrónico: marcos_palone@hotmail.com.
| Resumen |
Las fisuras orofaciales son un grupo de anomalías cuya etiología es resultante de la interacción entre factores genéticos y ambientales. Entre todos los genes candidatos para la ocurrencia de fisuras orofaciales no sindrómicas, el más citado y conocido es el IRF6; otros genes importantes son el FOXE1, PVRL1 y el MSX1. A partir de nuevos datos consolidados referentes a esta etiología, se puede establecer un sistema más efectivo de orientación genética para prevenir la ocurrencia de estos tipos de anomalías.
Palabras clave: Labio leporino; Fisura del paladar; Etiología; Genética (DeCS).
Tovani-Palone MR, Saldias-Vargas VP. Factores genéticos y fisuras orofaciales no sindrómicas. Rev. Fac. Med. 2016;64(2):381-3. Spanish. doi: https://doi.org/10.15446/revfacmed.v64n2.53551.
Abstract
Orofacial clefts are a group of anomalies whose etiology derives from the interaction between genetic and environmental factors. Among all candidate genes for the occurrence of nonsyndromic orofacial clefts, IRF6 is the most quoted and known. Other important genes are FOXE1, PVRL1 and MSX1. Thus, from new consolidated data for this etiology a more effective system of genetic counseling can be established to prevent the occurrence of these types of anomalies.
Keywords: Cleft lip; Cleft palate; Etiology; Genetics (MeSH).
Tovani-Palone MR, Saldias-Vargas VP. [Genetic Factors and Nonsyndromic Orofacial Clefts]. Rev. Fac. Med. 2016;64(2):381-3. Spanish. doi: https://doi.org/10.15446/revfacmed.v64n2.53551.
Las fisuras orofaciales son las malformaciones craneofaciales más comúnmente encontradas en la especie humana con una prevalencia mundial estimada de 1 por 700 individuos nacidos vivos (1). Se trata de un grupo de anomalías cuya etiología es caracterizada por un espectro de naturaleza multifactorial resultante de la interacción entre factores genéticos y ambientales (Figura 1) (1-3).
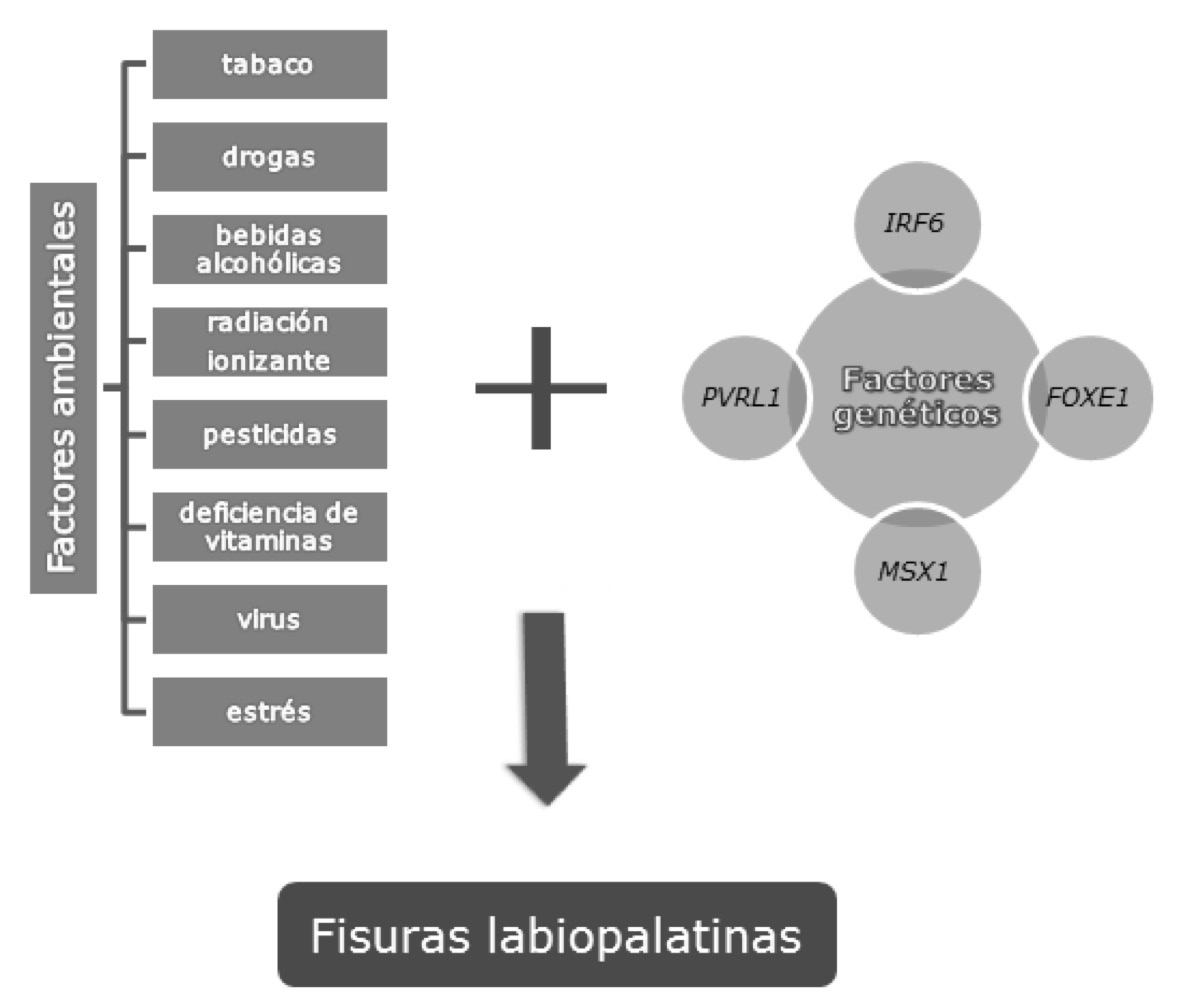
Figura 1. Principales elementos de la etiología de las fisuras labiopalatinas. Fuente: Elaboración con base en Rahimov et al. (4) y Garib et al. (5).
Es de resaltar que diversos estudios asocian los factores genéticos con el desarrollo de fisuras orofaciales (1-5) y establecen una ocurrencia estimada entre 60% y 70% de casos como aislados, sin ninguna combinación con síndromes u otras malformaciones (2,6).
Este trabajo tuvo como objetivo delimitar, de manera breve, las principales asociaciones existentes en la literatura vigente entre fisuras orofaciales no sindrómicas y los principales factores genéticos relacionados.
Por tratarse del que presenta mayor relación con la ocurrencia de fisuras y por estar involucrado en cerca de 12% de los casos de fisuras orofaciales no sindrómicas (1), el gen más citado y conocido entre todos los candidatos para la ocurrencia de estas malformaciones en la actualidad es el IRF6; además, este participa activamente en el desarrollo del síndrome de van der Woude y del Pterigeon Poplíteo (7). Otros genes importantes que merecen destaque son el FOXE1, involucrado directamente con el desarrollo embrionario; el PVRL1, decodificador de moléculas de adhesión celular, y el MSX1, decodificador de factores de transcripción e involucrado en la etiología de las agenesias dentarias. Aunque menos relevantes, otros genes candidatos al desarrollo de fisuras labiopalatinas son TGFA, TGFB2, TGFB3, FGF, GLI2, JAG2, SATB2, LHX8, SKI, ERBB2, SPRY2, TBX10 y MSX2 (1,4).
Adicionalmente, en vista de la alta prevalencia de defectos de esmalte dentario en individuos con fisuras orofaciales (8), cabe destacar que un estudio reciente realizado por Oliveira et al. (9), el cual investigó sobre mutaciones del gen AMELX en individuos con fisuras orofaciales y defectos en el esmalte dentario y sugiere que el respectivo gen es un posible candidato para el acontecimiento de estos tipos de anomalía craneofaciale.
Dada la gran diversidad fenotípica encontrada para las fisuras orofaciales (10), especialmente en los casos más graves, es posible presuponer que estas malformaciones derivan de interacciones conjuntas entre los diferentes genes implicados en la constitución de un cierto genotipo (1,4); sin embargo, todavía son recientes los hallazgos en estudios que tornan posible una investigación más concreta y conclusiva sobre su relación exacta, inclusive con los factores ambientales (2,5).
Siendo así, nuevos estudios que contemplan este tema representan conocimientos de alta importancia para que a partir de datos consolidados referentes a esta etiología pueda ser establecido un sistema efectivo de orientación genética con el objetivo principal de prevenir la ocurrencia de estos tipos de anomalías.
Conflicto de intereses
Ninguno declarado por los autores.
Financiación
Ninguna declarada por los autores.
Agradecimientos
Ninguno declarado por los autores.
Referencias
1. Palone MRT, Silva TR, Vargas VPS, Dalben GS. A relação do gene IRF6 com a ocorrência de fissura labiopalatina. Rev Fac Ciênc Méd Sorocaba. 2015;17(2):107-8.
2. Dixon MJ, Marazita ML, Beaty TH, Murray JC. Cleft lip and palate: understanding genetic and environmental influences. Nat. Rev. Genet. 2011;12(3):167-78.
http://doi.org/bv3wb4.
3. Farronato G, Cannalire P, Martinelli G, Tubertini I, Giannini L, Galbiati G, et al. Cleft lip and/or palate: review. Minerva Stomatol. 2014;63(4):111-26.
4. Rahimov F, Jugessur A, Murray JC. Genetics of nonsyndromic orofacial clefts. Cleft Palate Craniofac. J. 2012;49(1):73-91. http://doi.org/crk4dt.
5. Garib DG, Silva Filho OG, Janson G, Pinto JHN. Etiologia das más oclusões: perspectiva clínica (parte III)-fissuras labiopalatinas. Rev. Clín. Ortod. Dental Press. 2010;9(4):30-6.
6. Freitas JAS, Neves LT, Almeida ALPF, Garib DG, Trindade-Suedam IK, Yaedú RYF, et al. Rehabilitative treatment of cleft lip and palate: experience of the Hospital for Rehabilitation of Craniofacial Anomalies/USP (HRAC/USP) - Part 1: overall aspects. J. Appl. Oral Sci. 2012;20(1):9-15. http://doi.org/837.
7. Butali A, Mossey PA, Adeyemo WL, Eshete MA, Gaines LA, Even D, et al. Novel IRF6 mutations in families with Van Der Woude syndrome and popliteal pterygium syndrome from sub-Saharan Africa. Mol. Genet. Genomic. Med. 2014;2(3):254-60. http://doi.org/bhft.
8. Saldias-Vargas VP, Tovani-Palone MR, Moura-Martins AP, da Silva-Dalben G, Ribeiro-Gomide M. Enamel defects in permanent first molars and incisors in individuals with cleft lip and/or palate. Rev. Fac. Med. 2014;62(4):515-9. http://doi.org/bhfv.
9. Oliveira FV, Dionísio TJ, Neves LT, Machado MAAM, Santos CF, Oliveira TM. Amelogenin gene influence on enamel defects of cleft lip and palate patients. Braz. Oral Res. 2014; 28(1): 1-7. http://doi.org/bhfw.
10. Collins A, Arias L, Pengelly R, Martínez J, Briceño I, Ennis S. The potential for next generation sequencing to characterise the genetic variation underlying non-syndromic cleft lip and palate phenotypes. OA Genetics. 2013;1(1):10. http://doi.org/bhfz.
Ingrid Yoryeth Bastidas Pedreros
“Ejercicios de ilustración anatómica”
Universidad Nacional de Colombia
Referencias
Palone MRT, Silva TR, Vargas VPS, Dalben GS. A relação do gene IRF6 com a ocorrência de fissura labiopalatina. Rev Fac Ciênc Méd Sorocaba. 2015;17(2):107-8.
Dixon MJ, Marazita ML, Beaty TH, Murray JC. Cleft lip and palate: understanding genetic and environmental influences. Nat. Rev. Genet. 2011;12(3):167-78. http://doi.org/bv3wb4.
Farronato G, Cannalire P, Martinelli G, Tubertini I, Giannini L, Galbiati G, et al. Cleft lip and/or palate: review. Minerva Stomatol. 2014;63(4):111-26.
Rahimov F, Jugessur A, Murray JC. Genetics of nonsyndromic orofacial clefts. Cleft Palate Craniofac. J. 2012;49(1):73-91. http://doi.org/crk4dt.
Garib DG, Silva Filho OG, Janson G, Pinto JHN. Etiologia das más oclusões: perspectiva clínica (parte III)-fissuras labiopalatinas. Rev. Clín. Ortod. Dental Press. 2010;9(4):30-6.
Freitas JAS, Neves LT, Almeida ALPF, Garib DG, Trindade-Suedam IK, Yaedú RYF, et al. Rehabilitative treatment of cleft lip and palate: experience of the Hospital for Rehabilitation of Craniofacial Anomalies/USP (HRAC/USP) - Part 1: overall aspects. J. Appl. Oral Sci. 2012;20(1):9-15. http://doi.org/837.
Butali A, Mossey PA, Adeyemo WL, Eshete MA, Gaines LA, Even D, et al. Novel IRF6 mutations in families with Van Der Woude syndrome and popliteal pterygium syndrome from sub-Saharan Africa. Mol. Genet. Genomic. Med. 2014;2(3):254-60. http://doi.org/bhft.
Saldias-Vargas VP, Tovani-Palone MR, Moura-Martins AP, da Silva-Dalben G, Ribeiro-Gomide M. Enamel defects in permanent first molars and incisors in individuals with cleft lip and/or palate. Rev. Fac. Med. 2014;62(4):515-9. http://doi.org/bhfv.
Oliveira FV, Dionísio TJ, Neves LT, Machado MAAM, Santos CF, Oliveira TM. Amelogenin gene influence on enamel defects of cleft lip and palate patients. Braz. Oral Res. 2014; 28(1): 1-7. http://doi.org/bhfw.
Collins A, Arias L, Pengelly R, Martínez J, Briceño I, Ennis S. The potential for next generation sequencing to characterise the genetic variation underlying non-syndromic cleft lip and palate phenotypes. OA Genetics. 2013;1(1):10. http://doi.org/bhfz.
Cómo citar
APA
ACM
ACS
ABNT
Chicago
Harvard
IEEE
MLA
Turabian
Vancouver
Descargar cita
CrossRef Cited-by
1. Sophie Butterworth, Stephanie van Eeden, Hayley Llandro, David C.G. Sainsbury, Lucy Burbridge, Erfan Shamsoddin, Thomas Franchi, Pritik A Shah, Marcos Roberto Tovani Palone. (2024). Recent Advances in the Treatment of Orofacial Clefts. https://doi.org/10.5772/intechopen.108969.
Dimensions
PlumX
Visitas a la página del resumen del artículo
Descargas
Licencia
Derechos de autor 2016 Revista de la Facultad de Medicina

Esta obra está bajo una licencia Creative Commons Reconocimiento 3.0 Unported.
-





















